CHEK2 - CHEK2
CHEK2 ( Checkpoint quinase 2 ) é um gene supressor de tumor que codifica a proteína CHK2 , uma serina-treonina quinase . O CHK2 está envolvido no reparo do DNA , na parada do ciclo celular ou na apoptose em resposta a danos no DNA. Mutações no gene CHEK2 têm sido associadas a uma ampla gama de cânceres .
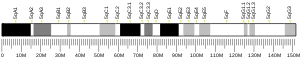
Localização do gene
O gene CHEK2 está localizado no braço longo (q) do cromossomo 22 na posição 12.1. Sua localização no cromossomo 22 se estende do par de bases 28.687.742 ao par de bases 28.741.904.
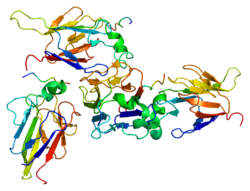
Estrutura da proteína
A proteína CHEK2 codificada pelo gene CHEK2 é uma serina treonina quinase . A proteína consiste em 543 aminoácidos e nos seguintes domínios :
- Domínio de cluster N-terminal SQ / TQ (SCD)
- Domínio associado a forkhead central (FHA)
- Domínio de serina / treonina quinase C-terminal (KD)
O domínio SCD contém vários motivos SQ / TQ que servem como locais para fosforilação em resposta a danos no DNA . O sítio mais notável e freqüentemente fosforilado sendo Thr68.
CHK2 aparece como um monômero em seu estado inativo. No entanto, no caso de dano ao DNA, a fosforilação de SCD causa dimerização de CHK2 . O Thr68 fosforilado (localizado no SCD) interage com o domínio FHA para formar o dímero . Após a dimerização da proteína, o KD é ativado por meio de autofosforilação. Uma vez que o KD é ativado, o dímero CHK2 se dissocia.
Função e mecanismo
O gene CHEK2 codifica para o checkpoint quinase 2 (CHK2), uma proteína que atua como supressor de tumor . CHK2 regula a divisão celular e tem a capacidade de impedir que as células se dividam muito rapidamente ou de maneira descontrolada.
Quando o DNA sofre uma quebra de fita dupla, o CHK2 é ativado. Especificamente, a proteína da família da fosfatidilinositol quinase ( PIKK ) ATM ativada por dano ao DNA fosforila o local Thr68 e ativa a CHK2. Uma vez ativado, o CHK2 fosforila alvos a jusante, incluindo as fosfatases CDC25 , responsáveis pela desfosforilação e ativação das quinases dependentes de ciclina (CDKs). Assim, a inibição de CHK2 das fosfatases CDC25 impede a entrada da célula na mitose . Além disso, a proteína CHK2 interage com várias outras proteínas, incluindo p53 (p53). A estabilização de p53 por CHK2 leva à interrupção do ciclo celular na fase G1 . Além disso, CHK2 é conhecido por fosforilar o fator de transcrição do ciclo celular E2F1 e a proteína de leucemia promielocítica (PML) envolvida na apoptose (morte celular programada).
Associação com câncer
A proteína CHK2 desempenha um papel crítico no ponto de verificação de danos ao DNA. Assim, as mutações no gene CHEK2 foram marcadas como causas para uma ampla gama de cânceres.
Em 1999, variações genéticas de CHEK2 foram encontradas para corresponder à suscetibilidade hereditária ao câncer.
Bell et al. (1999) descobriram três mutações da linha germinativa CHEK2 entre quatro famílias da síndrome de Li – Fraumeni (LFS) e 18 famílias semelhantes a Li – Fraumeni (LFL). Desde o tempo desta descoberta, duas das três variantes (uma deleção no domínio quinase no exon 10 e uma mutação missense no domínio FHA no exon 3) foram associadas à suscetibilidade herdada ao câncer de mama, bem como a outros cânceres.
Além das especulações iniciais, a triagem de pacientes LFS e LFL revelou nenhuma ou muito raras variantes individuais missense no gene CHEK2. Além disso, a deleção no domínio da quinase no exon 10 foi encontrada rara entre os pacientes LFS / LFL. As evidências desses estudos sugerem que CHEK2 não é um gene de predisposição para a síndrome de Li – Fraumeni.
Câncer de mama
Mutações herdadas no gene CHEK2 foram associadas a certos casos de câncer de mama . Mais notavelmente, a deleção de um único nucleotídeo de DNA na posição 1100 no exon 10 (1100delC) produz uma versão não funcional da proteína CHK2, truncada no domínio quinase. A perda da função normal da proteína CHK2 leva à divisão celular desregulada, dano acumulado ao DNA e, em muitos casos, ao desenvolvimento de tumor . A mutação CHEK2 * 1100del é mais comumente vista em indivíduos de ascendência do Leste e do Norte da Europa. Nessas populações, a mutação CHEK2 * 1100delC é observada em 1 em 100 a 1 em 200 indivíduos. No entanto, na América do Norte, a frequência cai para 1 em 333 para 1 em 500. A mutação está quase ausente na Espanha e na Índia. Estudos mostram que um CHEK2 1100delC corresponde a um risco duas vezes maior de câncer de mama e um risco 10 vezes maior de câncer de mama em homens.
Uma mutação CHEK2 conhecida como variante I157T do domínio FHA no exon 3 também foi associada ao câncer de mama, mas com um risco menor do que a mutação CHEK2 * 1100delC. A fração estimada de câncer de mama atribuída a essa variante é relatada em cerca de 1,2% nos Estados Unidos.
Mais duas mutações no gene CHEK2, CHEK2 * S428F, uma substituição de aminoácido para o domínio quinase no exon 11 e CHEK2 * P85L, uma substituição de aminoácido na região N-terminal (exon 1), foram encontradas na população judaica Ashkenazi . A sugestão de uma mutação fundadora hispânica também foi descrita.
Outros cânceres
Mutações em CHEK2 foram encontradas em casos de câncer hereditários e não hereditários. Estudos associam a mutação a casos de câncer de próstata , pulmão , cólon , rim e tireóide . Links também foram traçados para certos tumores cerebrais e osteossarcoma .
Ao contrário das mutações BRCA1 e BRCA2 , as mutações CHEK2 não parecem causar um risco elevado de câncer de ovário . No entanto, uma associação de grande efeito em todo o genoma para câncer de pulmão escamoso foi descrita para uma variante rara em CHEK2 (p.Ile157Thr, rs17879961, OR = 0,38).
Meiose
CHEK2 regula a progressão do ciclo celular e a montagem do fuso durante a maturação do oócito do camundongo e o desenvolvimento inicial do embrião . Embora CHEK2 seja um efetor a jusante da ATM quinase que responde principalmente a quebras de fita dupla, ela também pode ser ativada por ATR (ataxia-telangiectasia e relacionada com Rad3) quinase que responde principalmente a quebras de fita simples. Em camundongos, CHEK2 é essencial para a vigilância de danos ao DNA na meiose feminina . A resposta dos oócitos ao dano por quebra da fita dupla do DNA envolve uma hierarquia de vias na qual a quinase ATR sinaliza para CHEK2, que então ativa as proteínas p53 e p63 .
Na mosca da fruta Drosophila , a irradiação de células da linha germinativa gera quebras de fita dupla que resultam em parada do ciclo celular e apoptose . O ortólogo Drosophila CHEK2 mnk e o ortólogo p53 dp53 são necessários para grande parte da morte celular observada no início da oogênese, quando ocorre a seleção de oócitos e a recombinação meiótica.
Interações
Foi demonstrado que CHEK2 interage com:
Referências
Leitura adicional
- Caspari T (abril de 2000). "Como ativar o p53" . Biologia atual . 10 (8): R315-7. doi : 10.1016 / S0960-9822 (00) 00439-5 . PMID 10801407 . S2CID 17342787 .
- McGowan CH (junho de 2002). "Verificando Cds1 (Chk2): Um checkpoint quinase e supressor de tumor". BioEssays . 24 (6): 502–11. doi : 10.1002 / bies.10101 . PMID 12111733 . S2CID 6654874 .
- Honrado E, Osorio A, Palacios J, Benitez J (setembro de 2006). "Patologia e expressão gênica de tumores de mama hereditários associados com mutações do gene BRCA1, BRCA2 e CHEK2" . Oncogene . 25 (43): 5837–45. doi : 10.1038 / sj.onc.1209875 . PMID 16998498 . S2CID 20960561 .
- Nevanlinna H, Bartek J (setembro de 2006). "O gene CHEK2 e a suscetibilidade herdada ao câncer de mama" . Oncogene . 25 (43): 5912–9. doi : 10.1038 / sj.onc.1209877 . PMID 16998506 .
- Peng CY, Graves PR, Thoma RS, Wu Z, Shaw AS, Piwnica-Worms H (setembro de 1997). "Controle de ponto de verificação mitótico e G2: regulação da ligação da proteína 14-3-3 por fosforilação de Cdc25C em serina-216". Ciência . 277 (5331): 1501–5. doi : 10.1126 / science.277.5331.1501 . PMID 9278512 .
- Lykidis A, Jackson PD, Rock CO, Jackowski S (dezembro de 1997). "O papel da CDP-diacilglicerol sintetase e níveis de atividade da fosfatidilinositol sintase na regulação do conteúdo de fosfatidilinositol celular" . The Journal of Biological Chemistry . 272 (52): 33402–9. doi : 10.1074 / jbc.272.52.33402 . PMID 9407135 .
- Lindsay HD, DJ Griffiths, Edwards RJ, Christensen PU, Murray JM, Osman F, et al. (Fevereiro de 1998). "A ativação específica da fase S da cinase Cds1 define uma via secundária da resposta do ponto de verificação em Schizosaccharomyces pombe" . Genes e desenvolvimento . 12 (3): 382–95. doi : 10.1101 / gad.12.3.382 . PMC 316487 . PMID 9450932 .
- Matsuoka S, Huang M, Elledge SJ (dezembro de 1998). Ligação de ATM para a regulação do ciclo celular pela proteína quinase Chk2 ". Ciência . 282 (5395): 1893–7. Bibcode : 1998Sci ... 282.1893M . doi : 10.1126 / science.282.5395.1893 . PMID 9836640 .
- Martinho RG, Lindsay HD, Flaggs G, DeMaggio AJ, Hoekstra MF, Carr AM, Bentley NJ (dezembro de 1998). "A análise das proteínas quinases Rad3 e Chk1 define diferentes respostas de checkpoint" . The EMBO Journal . 17 (24): 7239–49. doi : 10.1093 / emboj / 17.24.7239 . PMC 1171070 . PMID 9857181 .
- Blasina A, de Weyer IV, Laus MC, Luyten WH, Parker AE, McGowan CH (janeiro de 1999). "Um homólogo humano do checkpoint quinase Cds1 inibe diretamente a Cdc25 fosfatase" . Biologia atual . 9 (1): 1–10. doi : 10.1016 / S0960-9822 (99) 80041-4 . PMID 9889122 . S2CID 18008732 .
- Brown AL, Lee CH, Schwarz JK, Mitiku N, Piwnica-Worms H, Chung JH (março de 1999). "Uma quinase relacionada ao Cds1 humano que funciona a jusante da proteína ATM na resposta celular ao dano ao DNA" . Anais da Academia Nacional de Ciências dos Estados Unidos da América . 96 (7): 3745–50. Bibcode : 1999PNAS ... 96.3745B . doi : 10.1073 / pnas.96.7.3745 . PMC 22365 . PMID 10097108 .
- Chaturvedi P, Eng WK, Zhu Y, Mattern MR, Mishra R, Hurle MR, et al. (Julho de 1999). "Mammalian Chk2 é um efetor a jusante da via do ponto de verificação de dano de DNA dependente de ATM" . Oncogene . 18 (28): 4047–54. doi : 10.1038 / sj.onc.1202925 . PMID 10435585 . S2CID 23907734 .
- Ouyang B, Li W, Pan H, Meadows J, Hoffmann I, Dai W (outubro de 1999). "A associação física e fosforilação da proteína fosfatase Cdc25C por Prk" . Oncogene . 18 (44): 6029–36. doi : 10.1038 / sj.onc.1202983 . PMID 10557092 .
- Dunham I, Shimizu N, Roe BA, Chissoe S, Hunt AR, Collins JE, et al. (Dezembro de 1999). "A sequência de DNA do cromossomo humano 22" . Nature . 402 (6761): 489–95. Bibcode : 1999Natur.402..489D . doi : 10.1038 / 990031 . PMID 10591208 .
- Bell DW, Varley JM, Szydlo TE, Kang DH, Wahrer DC, Shannon KE, et al. (Dezembro de 1999). "Mutações de hCHK2 da linha germinal heterozigótica na síndrome de Li-Fraumeni". Ciência . 286 (5449): 2528–31. doi : 10.1126 / science.286.5449.2528 . PMID 10617473 .
- Chehab NH, Malikzay A, Appel M, Halazonetis TD (fevereiro de 2000). "Chk2 / hCds1 funciona como um ponto de verificação de danos ao DNA em G (1) ao estabilizar o p53" . Genes e desenvolvimento . 14 (3): 278–88. doi : 10.1101 / gad.14.3.278 (inativo em 31 de maio de 2021). PMC 316357 . PMID 10673500 .Manutenção do CS1: DOI inativo em maio de 2021 ( link )
- Hirao A, Kong YY, Matsuoka S, Wakeham A, Ruland J, Yoshida H, et al. (Março de 2000). "Ativação induzida por danos no DNA de p53 pelo checkpoint quinase Chk2". Ciência . 287 (5459): 1824–7. Bibcode : 2000Sci ... 287.1824H . doi : 10.1126 / science.287.5459.1824 . PMID 10710310 .
- Lee JS, Collins KM, Brown AL, Lee CH, Chung JH (março de 2000). "A fosforilação mediada por hCds1 de BRCA1 regula a resposta a danos no DNA". Nature . 404 (6774): 201–4. Bibcode : 2000Natur.404..201L . doi : 10.1038 / 35004614 . PMID 10724175 . S2CID 4345911 .
- Zhou BB, Chaturvedi P, Spring K, Scott SP, Johanson RA, Mishra R, et al. (Abril de 2000). "A cafeína abole o ponto de verificação de danos ao DNA G (2) / M dos mamíferos ao inibir a atividade da quinase mutada da ataxia-telangiectasia" . The Journal of Biological Chemistry . 275 (14): 10342–8. doi : 10.1074 / jbc.275.14.10342 . PMID 10744722 . S2CID 4240483 .
links externos
- Recursos educacionais arquivados em 13-04-2010 na Wayback Machine
- Críticas Gene
- Testes Genéticos
- CHEK2 + proteína, + humano na Biblioteca Nacional de Medicina dos Estados Unidos Medical Subject Headings (MeSH)
- Localização do genoma humano CDS1 e página de detalhes do gene CDS1 no navegador do genoma UCSC .
- Human CHEK2 localização genoma e CHEK2 gene detalhes da página no navegador UCSC Genome .
Este artigo incorpora texto da Biblioteca Nacional de Medicina dos Estados Unidos , que é de domínio público .