Cromossomo 5 - Chromosome 5
| Cromossomo 5 | |
|---|---|
 Cromossoma humano 5 par depois L-bandas .
Um é da mãe, outro é do pai. | |
 Par do cromossomo 5
no cariograma masculino humano . | |
| Recursos | |
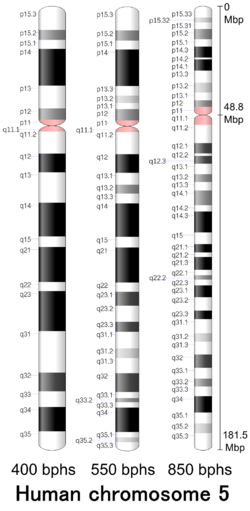
| Comprimento ( bp ) | 181.538.259 bp ( GRCh38 ) |
| No. de genes | 839 ( CCDS ) |
| Modelo | Autossomo |
| Posição do centrômero |
Submetacêntrico (48,8 Mbp) |
| Listas completas de genes | |
| CCDS | Lista de genes |
| HGNC | Lista de genes |
| UniProt | Lista de genes |
| NCBI | Lista de genes |
| Visualizadores de mapa externos | |
| Conjunto | Cromossomo 5 |
| Entrez | Cromossomo 5 |
| NCBI | Cromossomo 5 |
| UCSC | Cromossomo 5 |
| Sequências completas de DNA | |
| RefSeq | NC_000005 ( FASTA ) |
| GenBank | CM000667 ( FASTA ) |
O cromossomo 5 é um dos 23 pares de cromossomos em humanos . As pessoas normalmente têm duas cópias desse cromossomo. O cromossomo 5 abrange cerca de 181 milhões de pares de bases (os blocos de construção do DNA ) e representa quase 6% do DNA total nas células . O cromossomo 5 é o quinto maior cromossomo humano, embora tenha uma das menores densidades gênicas . Isso é parcialmente explicado por numerosas regiões pobres em genes que exibem um grau notável de não codificação e conservação sintênica com vertebrados não mamíferos , sugerindo que eles são funcionalmente restritos.
Como o cromossomo 5 é responsável por muitas formas de crescimento e desenvolvimento (divisões celulares), as alterações podem causar câncer. Um exemplo seria a leucemia mieloide aguda (LMA).
Genes
Número de genes
A seguir estão algumas das estimativas de contagem de genes do cromossomo humano 5. Como os pesquisadores usam diferentes abordagens para a anotação do genoma, suas previsões do número de genes em cada cromossomo variam (para obter detalhes técnicos, consulte previsão de genes ). Entre vários projetos, o projeto de sequência de codificação de consenso colaborativo ( CCDS ) adota uma estratégia extremamente conservadora. Portanto, a previsão do número do gene do CCDS representa um limite inferior no número total de genes codificadores de proteínas humanas.
| Estimado por | Genes codificadores de proteínas | Genes de RNA não codificantes | Pseudogenes | Fonte | Data de lançamento |
|---|---|---|---|---|---|
| CCDS | 839 | - | - | 08/09/2016 | |
| HGNC | 790 | 355 | 574 | 12/05/2017 | |
| Conjunto | 882 | 1.207 | 707 | 29-03-2017 | |
| UniProt | 875 | - | - | 28/02/2018 | |
| NCBI | 886 | 981 | 785 | 19/05/2017 |
Lista de genes
A seguir está uma lista parcial de genes no cromossomo humano 5. Para obter a lista completa, consulte o link na caixa de informações à direita.
- ABLIM3 : proteína 3 que codifica a proteína LIM de ligação à actina
- ADAMTS2 : ADAM metalopeptidase com motivo de trombospondina tipo 1, 2
- AGXT2 : Alanina-glioxilato aminotransferase 2
- ANKRD31 : codificação do domínio de repetição 31 da proteína Anquirina
- Apbb3 : que codifica a proteína amilóide beta A4 precursor membro da família B-proteína de ligação 3
- APC : adenomatose polipose coli
- ARL15 : codificação da proteína ADP-fator de ribosilação 15
- BRIX1 : homólogo da proteína da biogênese do ribossomo BRX1 (também BXDC2)
- C1QTNF3 : Proteína 3 relacionada ao fator de necrose tumoral C1q do complemento
- FAM114A2 : proteína que codifica FAM114A2
- NREP : proteína relacionada à regeneração neuronal
- FAM172A : proteína que codifica a proteína UPF0528 FAM172A
- CPLANE1 : Ciliogênese e efetor de polaridade plana 1
- CAST : calpastatina
- CPLX2 : Complexin-2
- CREBRF : fator regulador da proteína de codificação CREB3
- CXXC5 : proteína de dedo zing 5 do tipo CXXC
- DPYSL3 : Proteína 3 semelhante a dihidropirimidinase
- EGR1 : proteína 1 de resposta ao crescimento inicial
- ERAP1 : retículo endoplasmático aminopeptidase 1 (anteriormente denominado ARTS-1 )
- ERAP2 : retículo endoplasmático aminopeptidase 2
- ESM1 : Molécula 1 específica para células endoteliais
- DTDST : transportador de sulfato de displasia diastrófica
- EIF4E1B : que codifica a proteína eucariótica do fator de iniciação da tradução 4E membro da família 1B
- ERCC8 : deficiência de reparação de roedores de complementação cruzada de reparo por excisão, grupo de complementação 8
- FAM71B : Família de proteínas codificadoras com similaridade de sequência 71 membro B
- FAM105B : codificando a família de proteínas com semelhança de sequência 105, membro B
- FASTKD3 : proteína 3 contendo domínio de quinase FAST
- FBXL7 : proteína 7 de repetição de F-box / LRR
- FCHSD1 : FCH e proteína 1 de domínio SH3 duplo
- FGF1 : fator de crescimento de fibroblastos 1 (fator de crescimento de fibroblastos ácido)
- FGFR4 : receptor 4 do fator de crescimento de fibroblastos
- GM2A : ativador gangliosídeo GM2
- GNPDA1 : Glucosamina-6-fosfato isomerase 1
- GPBP1 : vasculina
- HEXB : hexosaminidase B (polipeptídeo beta)
- HMGXB3 : codificando a proteína HMG-box contendo 3
- IK : Proteína Vermelha
- IRX1 : proteína homeodomínio da classe Iroquois (humana)
- LARP1 : proteína 1 relacionada com La
- LMAN2 : Lectina manose ligação 2
- LNCR3 codificação de proteína susceptibilidade ao cancro do pulmão 3
- LPCAT1 : Lisofosfatidilcolina aciltransferase 1
- LYSMD3 : LysM e proteína 3 contendo domínio de ligação de peptidoglicano putativo
- MAN2A1 : Alfa-manosidase 2
- MASS1 : monogênico, homólogo de suscetibilidade a crises audiogênicas 1 (camundongo)
- MCC : proteína de câncer mutante colorretal
- MCCC2 : metilcrotonoil-Coenzima A carboxilase 2 (beta)
- MEF2C : Fator 2C potenciador específico de miócitos
- MEF2C-AS1 : codificando a proteína MEF2C antisense RNA 1
- MGAT1 : Manosil (alfa-1,3 -) - glicoproteína beta-1,2-N-acetilglucosaminiltransferase
- MIR146A : microRNA 146a
- MTRR : 5-metiltetraidrofolato-homocisteína metiltransferase redutase
- MZB1 : proteína específica da célula da zona B e B1 marginal
- NIPBL : homólogo Nipped-B (Drosophila)
- NSA2 codificação de proteína proteína nuclear TGF beta-1 induzível
- NSD1 : proteína co- reguladora da transcrição
- NSUN2 : família de domínio NOP2 / Sun, membro 2
- NR2F1 : receptor de hormônio nuclear
- NUDCD2 : proteína 2 contendo domínio NudC
- P4HA2 : subunidade alfa-2 da prolil 4-hidroxilase
- PCBD2 : Pterin-4-alfa-carbinolamina desidratase 2
- PELO : Homólogo de Pelota
- PHAX : adaptador fosforilado para exportação de RNA
- Pikachurin : Responsável pelo funcionamento das sinapses da fita ; permite que o olho rastreie objetos em movimento
- PFDN1 : Subunidade 1 de Prefoldina
- POLR3G : polipeptídeo G (32kD) da proteína polimerase (RNA) III (dirigida ao DNA)
- PPIP5K2 : difosfoinositol pentacisfosfato quinase 2
- PRCC1 : Bobina 1 rica em prolina
- PURA : proteína A de ligação ao elemento rico em purinas
- PWWP2A : codificação do domínio PWWP da proteína contendo 2A
- RANBP3L : que codifica a proteína de ligação a RAN de proteína 3 semelhante
- RMND5B : Necessário para homólogo B da divisão 5 nuclear meiótica
- SFXN1 : Sideroflexin-1
- SKIV2L2 : Ski2 como RNA helicase 2
- SLC22A5 : família de transportadores de soluto 22 (transportador de cátions orgânicos), membro 5
- SLC26A2 : família de transportador de soluto 26 (transportador de sulfato), membro 2
- SH3TC2 : repetições de domínio e tetratricopeptídeo 2
- SLCO4C1 : Membro da família do transportador de ânion orgânico transportador de soluto 4c1
- SLU7 : fator de processamento de pré-mRNA SLU7
- SMN1 : neurônio motor de sobrevivência 1, telomérico
- SMN2 : neurônio motor de sobrevivência 2, centromérico
- SNCAIP : sinucleína, proteína de interação alfa (sinfilina)
- SPEF2 : proteína flagelar 2 de esperma
- SPINK5 : inibidor de serina protease tipo Kazal 5 (LEKTI)
- SPINK6 : inibidor de serina protease tipo Kazal 6
- SPINK9 : inibidor de serina protease tipo Kazal 9 (LEKTI-2)
- SPZ1 : proteína zipper de leucina espermatogênica 1
- STC2 : Stanniocalcina-2
- TBCA : chaperona A específica de tubulina
- TCOF1 : síndrome de Treacher Collins-Franceschetti 1
- TGFBI : queratoepitelina
- THG1L : Provável tRNA (His) guanililtransferase
- TICAM2 : molécula adaptadora 2 contendo domínio TIR
- TNFAIP8 : Fator de necrose tumoral, proteína 8 induzida por alfa
- TTC37 : domínio de repetição de tetratricopeptídeo 37
- UPF0488 : codifica a via de sinalização da proteína do receptor acoplado à proteína G
- YIPF5 : membro da família 5 do domínio Yip1
- YTHDC2 : o domínio YTH da proteína codificadora contendo 2
- ZBED3 : proteína 3 contendo o domínio BED de dedo de zinco
- ZNF608 : que codifica a proteína de dedo de zinco 608
Doenças e distúrbios
A seguir estão algumas das doenças relacionadas aos genes localizados no cromossomo 5:
- Acondrogênese tipo 1B
- Atelosteogênese, tipo II
- Síndrome de atrofia óptica de Bosch-Boonstra-Schaaf
- Doença de Charcot-Marie-Tooth, tipo 4
- Síndrome de Cockayne
- Síndrome de Cornelia de Lange
- Distrofia da córnea da camada de Bowman
- Cri du chat
- Displasia diastrófica
- Síndrome de Ehlers-Danlos
- Polipose adenomatosa familiar
- Distrofia corneana granular tipo I
- Distrofia corneana granular tipo II
- GM2-gangliosidose, variante AB
- Homocistinúria
- Deficiência de 3-metilcrotonil-CoA carboxilase
- Síndrome mielodisplásica
- Síndrome de Netherton
- Dependência de nicotina
- Mal de Parkinson
- Deficiência de carnitina primária
- Displasia epifisária múltipla recessiva
- Doença de Sandhoff
- Atrofia muscular espinhal
- Síndrome de Sotos
- Atrofia muscular espinhal do neurônio motor de sobrevivência
- Síndrome de Treacher Collins
- Síndrome trico-hepato-entérica
- Síndrome de Usher
Condições cromossômicas
As seguintes condições são causadas por mudanças na estrutura ou número de cópias do cromossomo 5:
- A síndrome de Cri-du-chat é causada por uma deleção da extremidade do braço curto (p) do cromossomo 5. Essa alteração cromossômica é escrita como 5p-. Os sinais e sintomas da síndrome de cri-du-chat provavelmente estão relacionados à perda de múltiplos genes nessa região. Os pesquisadores não identificaram todos esses genes ou determinaram como sua perda leva às características do distúrbio. Eles descobriram, entretanto, que uma deleção maior tende a resultar em retardo mental mais grave e atrasos no desenvolvimento em pessoas com síndrome do cri-du-chat.
- Os pesquisadores definiram regiões estreitas do braço curto do cromossomo 5 que estão associadas a características particulares da síndrome do cri-du-chat. Uma região específica designada 5p15.3 está associada a um grito de gato, e uma região próxima chamada 5p15.2 está associada a retardo mental, cabeça pequena (microcefalia) e características faciais distintas.
- A polipose adenomatosa familiar é causada por uma deleção do gene supressor de tumor APC no braço longo (q) do cromossomo 5. Essa alteração cromossômica resulta em milhares de pólipos colônicos, o que dá ao paciente um risco de 100% de câncer de cólon se a colectomia total não for feito.
- A síndrome de deleção do cromossomo 5q é causada pela deleção do braço q (braço longo) do cromossomo 5. Essa deleção tem sido associada a várias doenças relacionadas ao sangue, incluindo síndrome mielodisplásica e eritroblastopenia . Esta é uma condição diferente da Cri-du-chat mencionada acima.
- Outras mudanças no número ou na estrutura do cromossomo 5 podem ter uma variedade de efeitos, incluindo crescimento e desenvolvimento retardados, características faciais distintas, defeitos de nascença e outros problemas médicos. Mudanças no cromossomo 5 incluem um segmento extra do braço curto (p) ou longo (q) do cromossomo em cada célula (trissomia parcial 5p ou 5q), um segmento ausente do braço longo do cromossomo em cada célula (monossomia parcial 5q), e uma estrutura circular chamada cromossomo em anel 5. Um cromossomo em anel ocorre quando ambas as extremidades de um cromossomo quebrado são reunidas.
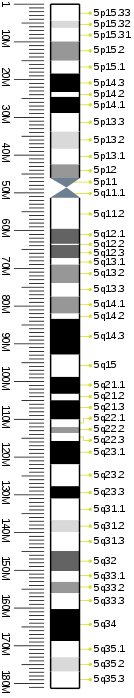
Banda citogenética
| Chr. | Braço | Banda | ISCN start |
Parada ISCN |
Basepair início |
Parada do basepair |
Mancha | Densidade |
|---|---|---|---|---|---|---|---|---|
| 5 | p | 15,33 | 0 | 278 | 1 | 4.400.000 | gneg | |
| 5 | p | 15,32 | 278 | 401 | 4.400.001 | 6.300.000 | gpos | 25 |
| 5 | p | 15,31 | 401 | 555 | 6.300.001 | 9.900.000 | gneg | |
| 5 | p | 15,2 | 555 | 802 | 9.900.001 | 15.000.000 | gpos | 50 |
| 5 | p | 15,1 | 802 | 972 | 15.000.001 | 18.400.000 | gneg | |
| 5 | p | 14,3 | 972 | 1234 | 18.400.001 | 23.300.000 | gpos | 100 |
| 5 | p | 14,2 | 1234 | 1281 | 23.300.001 | 24.600.000 | gneg | |
| 5 | p | 14,1 | 1281 | 1543 | 24.600.001 | 28.900.000 | gpos | 100 |
| 5 | p | 13,3 | 1543 | 1836 | 28.900.001 | 33.800.000 | gneg | |
| 5 | p | 13,2 | 1836 | 2068 | 33.800.001 | 38.400.000 | gpos | 25 |
| 5 | p | 13,1 | 2068 | 2253 | 38.400.001 | 42.500.000 | gneg | |
| 5 | p | 12 | 2253 | 2407 | 42.500.001 | 46.100.000 | gpos | 50 |
| 5 | p | 11 | 2407 | 2592 | 46.100.001 | 48.800.000 | acen | |
| 5 | q | 11,1 | 2592 | 2839 | 48.800.001 | 51.400.000 | acen | |
| 5 | q | 11,2 | 2839 | 3271 | 51.400.001 | 59.600.000 | gneg | |
| 5 | q | 12,1 | 3271 | 3518 | 59.600.001 | 63.600.000 | gpos | 75 |
| 5 | q | 12,2 | 3518 | 3580 | 63.600.001 | 63.900.000 | gneg | |
| 5 | q | 12,3 | 3580 | 3765 | 63.900.001 | 67.400.000 | gpos | 75 |
| 5 | q | 13,1 | 3765 | 4012 | 67.400.001 | 69.100.000 | gneg | |
| 5 | q | 13,2 | 4012 | 4197 | 69.100.001 | 74.000.000 | gpos | 50 |
| 5 | q | 13,3 | 4197 | 4397 | 74.000.001 | 77.600.000 | gneg | |
| 5 | q | 14,1 | 4397 | 4752 | 77.600.001 | 82.100.000 | gpos | 50 |
| 5 | q | 14,2 | 4752 | 4907 | 82.100.001 | 83.500.000 | gneg | |
| 5 | q | 14,3 | 4907 | 5400 | 83.500.001 | 93.000.000 | gpos | 100 |
| 5 | q | 15 | 5400 | 5678 | 93.000.001 | 98.900.000 | gneg | |
| 5 | q | 21,1 | 5678 | 5879 | 98.900.001 | 103.400.000 | gpos | 100 |
| 5 | q | 21,2 | 5879 | 5987 | 103.400.001 | 105.100.000 | gneg | |
| 5 | q | 21,3 | 5987 | 6295 | 105.100.001 | 110.200.000 | gpos | 100 |
| 5 | q | 22,1 | 6295 | 6419 | 110.200.001 | 112.200.000 | gneg | |
| 5 | q | 22,2 | 6419 | 6527 | 112.200.001 | 113.800.000 | gpos | 50 |
| 5 | q | 22,3 | 6527 | 6666 | 113.800.001 | 115.900.000 | gneg | |
| 5 | q | 23,1 | 6666 | 6943 | 115.900.001 | 122.100.000 | gpos | 100 |
| 5 | q | 23,2 | 6943 | 7267 | 122.100.001 | 127.900.000 | gneg | |
| 5 | q | 23,3 | 7267 | 7468 | 127.900.001 | 131.200.000 | gpos | 100 |
| 5 | q | 31,1 | 7468 | 7807 | 131.200.001 | 136.900.000 | gneg | |
| 5 | q | 31,2 | 7807 | 8008 | 136.900.001 | 140.100.000 | gpos | 25 |
| 5 | q | 31,3 | 8008 | 8316 | 140.100.001 | 145.100.000 | gneg | |
| 5 | q | 32 | 8316 | 8625 | 145.100.001 | 150.400.000 | gpos | 75 |
| 5 | q | 33,1 | 8625 | 8887 | 150.400.001 | 153.300.000 | gneg | |
| 5 | q | 33,2 | 8887 | 9072 | 153.300.001 | 156.300.000 | gpos | 50 |
| 5 | q | 33,3 | 9072 | 9304 | 156.300.001 | 160.500.000 | gneg | |
| 5 | q | 34 | 9304 | 9690 | 160.500.001 | 169.000.000 | gpos | 100 |
| 5 | q | 35,1 | 9690 | 9952 | 169.000.001 | 173.300.000 | gneg | |
| 5 | q | 35,2 | 9952 | 10183 | 173.300.001 | 177.100.000 | gpos | 25 |
| 5 | q | 35,3 | 10183 | 10600 | 177.100.001 | 181.538.259 | gneg |
Referências
Leitura adicional
- Mainardi PC, Perfumo C, Cali A, Coucourde G, Pastore G, Cavani S, Zara F, Overhauser J, Pierluigi M, Bricarelli FD (2001). "Caracterização clínica e molecular de 80 pacientes com deleção 5p: correlação genótipo-fenótipo" . J Med Genet . 38 (3): 151–8. doi : 10.1136 / jmg.38.3.151 . PMC 1734829 . PMID 11238681 .
- Schafer IA, Robin NH, Posch JJ, Clark BA, Izumo S, Schwartz S (2001). "Síndrome de deleção distal 5q: correlações fenotípicas". Am J Med Genet . 103 (1): 63–8. doi : 10.1002 / ajmg.1513 . PMID 11562936 .
- Schmutz J, Martin J, Terry A, Couronne O, Grimwood J, Lowry S, et al. (Setembro de 2004). "A sequência de DNA e análise comparativa do cromossomo 5 humano" . Nature . 431 (7006): 268–74. Bibcode : 2004Natur.431..268S . doi : 10.1038 / nature02919 . PMID 15372022 .
- Siddiqi R, Gilbert F (2003). "Cromossomo 5". Teste Genet . 7 (2): 169–87. doi : 10.1089 / 109065703322146902 . PMID 12885343 .
links externos
- Instituto Nacional de Saúde. "Cromossomo 5" . Referência de Genetics Home . Arquivado do original em 14 de outubro de 2004 . Recuperado em 06-05-2017 .
- "Cromossomo 5" . Arquivo de informações do projeto do genoma humano 1990–2003 . Recuperado em 06-05-2017 .